科技工作者之家
科界APP是专注科技人才,知识分享与人才交流的服务平台。
科技工作者之家 2018-11-07
内容来源:华中科技大学新闻网
新闻网讯(通讯员 谭重阳)10月5日,牛津大学出版社(Oxford University Press)出版的《Bioinformatics》(2017年影响因子5.481)在线发表了生命学院宁康教授团队的微生物亚种识别方法Strain-GeMS(https://github.com/HUST-NingKang-Lab/straingems)。
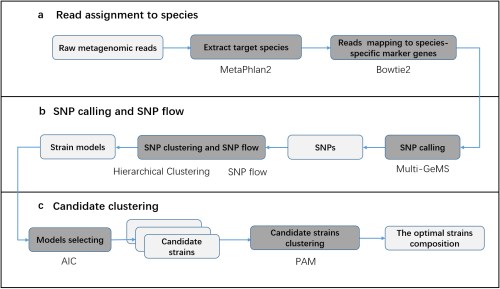
生命学院宁康教授为通讯作者,生命学院硕士生谭重阳和南开大学讲师崔巍为共同第一作者。在已亚种鉴定方法ConStrains的基础上,该团队通过完成Multi-GeMS与SNP-flow, PAM等的整合,提供了一个更为准确的微生物亚种识别方法。在模拟数据上将Strain-GeMS与其他一些已有方法ConStrains,Midas,Sigma做了比较,验证了其亚种识别的准确性。同时将Strain-GeMS应用到哈扎人肠道微生物数据上,揭示了亚种出现规律的季节性变化。
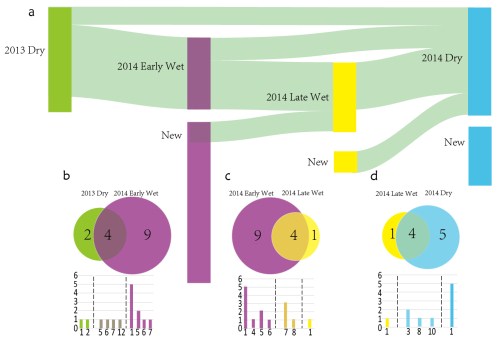
据了解,人类的许多疾病都与单个微生物或者一组微生物有关,如Ⅱ型糖尿病(T2D),肥胖症,癌症和一些免疫相关的疾病。同一物种内的不同菌株可能对人类健康产生完全不同的影响。例如,Escherichia coli O157:H7是一种高毒力大肠杆菌菌株,而大肠杆菌中的大多数其他菌株不是致病的。将亚种识别应用到人体肠道和各种环境微生物群落的分析上,将会使我们对不同环境下的微生物亚种存在情况,对亚种的地理分布、主导性与持续性产生全新的认识。通过对某些特定致病菌株的鉴定,还可以把亚种识别应用到流行病监测和医学诊断上,更好地服务于人类健康。
文章链接:https://academic.oup.com/bioinformatics/advance-article/doi/10.1093/bioinformatics/bty844/5116146?searchresult=1
来源:华中科技大学新闻网
原文链接:http://news.hust.edu.cn/info/1002/33176.htm
版权声明:除非特别注明,本站所载内容来源于互联网、微信公众号等公开渠道,不代表本站观点,仅供参考、交流、公益传播之目的。转载的稿件版权归原作者或机构所有,如有侵权,请联系删除。
电话:(010)86409582
邮箱:kejie@scimall.org.cn

全球微生物模式菌株基因组和微生物组测序合作计划正式启动
微生物组研究:关乎人类的未来
美国院士:强烈呼吁中国母亲不要给小孩滥用抗生素


微生物所发表中国微生物组数据平台
科普:夫妻相真的与细菌有关吗?




特别报道Nature丨人类微生物组计划之“微生物与炎症性肠病”
人类胎盘到底有没有微生物组?




人类微生物组影响健康机制揭秘
瘤胃微生物

青岛能源所开发出产油微生物菌株的高通量质谱筛选平台